4月27日,山东大学生命科学学院孙磊团队联合复旦大学杨禹丞团队和北京大学汪阳明团队在综合性期刊Nature Communications在线发表题为“Augmented prediction of multi-species protein–RNA interactions using evolutionary conservation of RNA-binding proteins”的研究论文,开发了一个用于跨物种RBP–RNA相互作用预测的人工智能算法MuSIC(Multi-Species RBP–RNA Interactions using Conservation)。

RNA结合蛋白(RBP)通过识别RNA参与转录、剪接和翻译等关键过程,其功能异常与癌症、神经退行性疾病等重大疾病密切相关。尽管小鼠、斑马鱼等模式生物广泛用于疾病机制和药物研究,目前RBP–RNA互作数据仍主要集中在人类,其他物种数据相对匮乏,限制了相关研究的深入开展。因此,开发跨物种RBP–RNA相互作用预测模型,有助于在数据稀缺的模式生物中准确预测RBP结合位点,推动RNA调控机制解析和疾病研究。
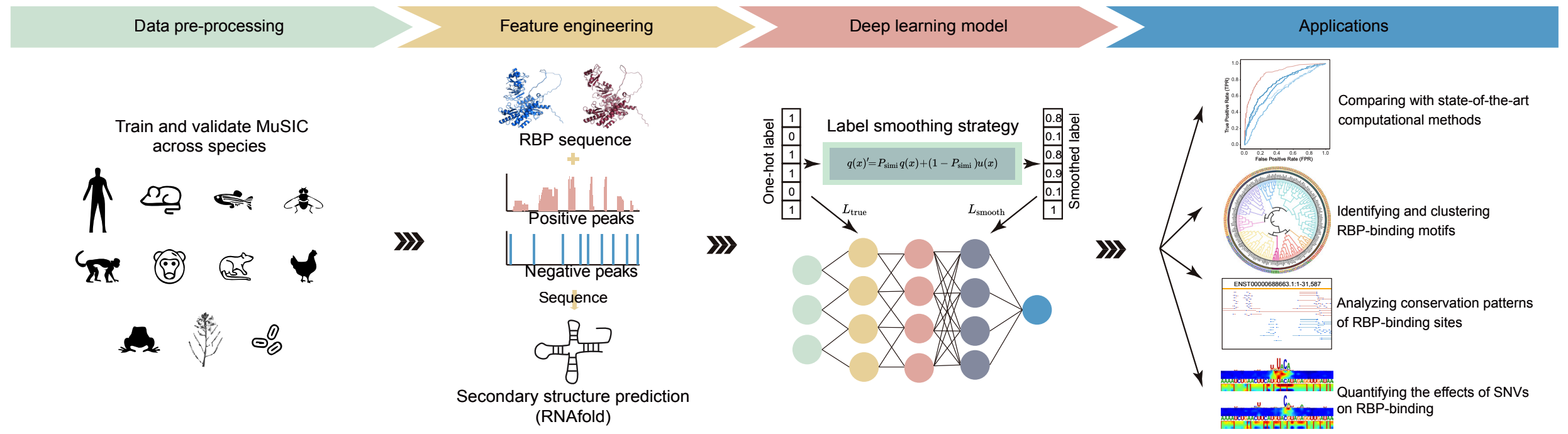
研究团队发现,RBP的核心RNA结合结构域及其RNA识别模式在进化过程中高度保守,提示RBP–RNA相互作用具有跨物种迁移的内在规律。基于这一发现,团队整合RBP保守性信息与RNA、蛋白预训练大模型特征,开发了跨物种RBP–RNA相互作用预测人工智能算法MuSIC(图1)。该模型在多物种预测中表现出优异的泛化能力,例如利用人类数据预测斑马鱼RBP结合偏好时,平均AUC达到0.83,明显优于现有方法(平局AUC=0.6)。此外,团队将MuSIC用于分析单核苷酸变异对RBP结合的影响,发现致病突变比良性突变更容易扰动RBP结合,并揭示这些受影响事件富集于泛素化调控等关键生物过程,提示遗传变异可能通过破坏RNA调控网络影响蛋白稳态并参与疾病发生。
山东大学生命科学学院硕士研究生何嘉乐、博士后周通、北京大学未来技术学院博士后胡鲁峰为共同第一作者,山东大学生命科学学院孙磊教授和复旦大学生物医学工程与技术创新学院杨禹丞副研究员为共同通讯作者,北京大学未来技术学院汪阳明教授对本研究有重要贡献。山东大学博士研究生焦玉华、本科生王峻昊、严晟文、贾思瑶、朱文韬,博士后陈秋臻,香港城市大学助理教授张继林,山东大学贾木天教授、李远宁教授、王显伟教授参与了本研究。研究得到了国家重点研发计划项目、国家自然科学基金和山东省自然科学基金等项目的资助。
MuSIC已经部署在交互式网站:https://sunlab.qd.sdu.edu.cn/MuSIC,欢迎大家使用。
论文链接: https://doi.org/10.1038/s41467-026-72351-6
