4月22日,山东大学生命科学学院郭卫华教授团队在国际知名期刊Genome Biology在线发表了题为“Single-cell and spatial transcriptomics in Phragmites australis reveal the associations of B chromosomes with plant invasiveness”的研究论文。该研究通过整合单细胞RNA测序与空间转录组学技术,构建了芦苇茎芽系统的单细胞分子图谱,发现北美入侵种群相比欧洲非入侵种群存在显著的B染色体拷贝数扩张,且B染色体上携带的SCC3、IMP-α3和GATA2等基因在入侵种群的多种细胞类型中普遍上调,为“B染色体驱动植物入侵能力增强”提供了直接的功能基因组学证据。

入侵植物对全球生物多样性构成严峻威胁,然而其成功入侵背后的分子与基因组学机制至今仍不明朗。芦苇(Phragmites australis)是全球分布最广的草本植物之一,在原产地欧洲广泛分布却不具入侵性;约200年前传入北美后,其迅速扩张蔓延,成为北美湿地生态系统中危害最为严重的入侵物种之一。与欧洲源种群相比,北美入侵种群在茎再生能力等生活史性状上表现出显著优势,为深入解析入侵机制提供了理想的比较研究系统。前期研究已发现,北美入侵种群普遍具有更大的基因组,B染色体积累与大量串联重复可能是基因组增大的主要驱动力,但其背后的功能机制尚不清楚。
该研究以地下茎萌发的新生茎芽为材料,对来自欧洲(非入侵)和北美(入侵)种群各三个个体共六个样本开展了单细胞RNA测序与空间转录组学分析。研究共捕获67,194个细胞,识别出19个转录组学上相互独立的细胞类群,涵盖分生组织细胞、薄壁组织、叶肉细胞、表皮细胞及维管组织等多种细胞类型,构建了迄今首个芦苇茎芽系统的单细胞分子图谱。研究进一步利用Tangram算法将单细胞数据投影至空间转录组数据,实现了各细胞类型的空间定位验证。在种群比较层面,入侵种群的薄壁组织、表皮、维管组织及叶肉细胞中普遍上调了与糖饥饿、缺光应答相关的基因;表皮细胞还表现出缺氧响应基因的强烈激活以及防御相关呼吸爆发基因的显著下调,与生活史权衡理论所预测的“以生长替代防御”策略高度吻合。值得注意的是,上调差异基因中有相当大比例位于B染色体上,其中叶肉细胞达21.2%,维管组织达20.2%,叶片转录组数据中更有46%的上调基因定位于B染色体。
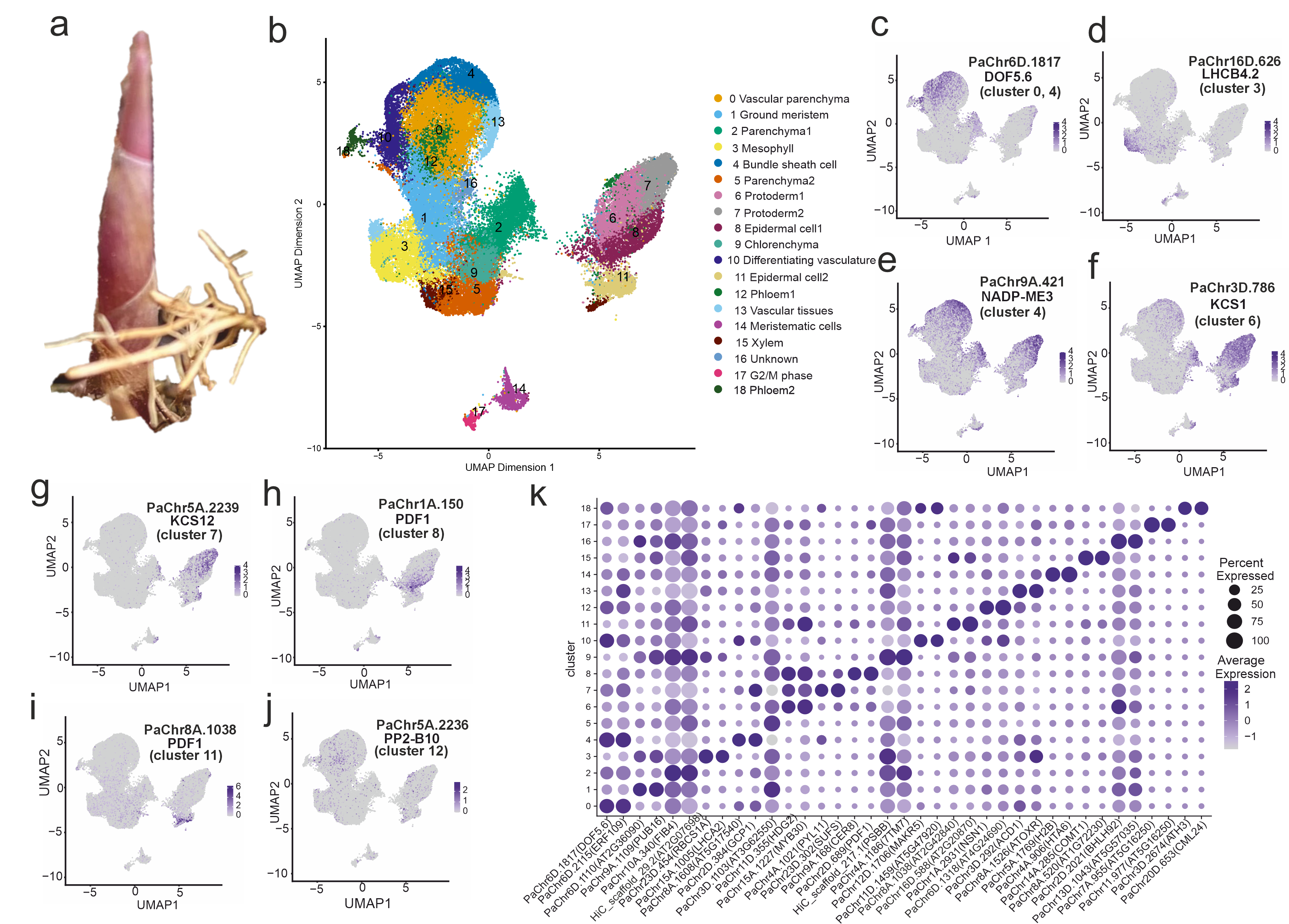
研究通过对88个全球采样个体的RAD测序数据及9个个体的全基因组测序数据进行分析,发现北美入侵种群B染色体与常染色体的测序深度比值平均为1.99(约相当于4条B染色体拷贝),而欧洲源种群该比值仅约0.26,两者差异显著。在B染色体差异表达基因中,SCC3(PaChr24B.240和PaChr24B.218)、IMP-α3(PaChr24B.43)和GATA2(PaChr24B.82)三个基因在入侵种群几乎所有细胞类型中均高度上调,是跨细胞类型最为稳定表达的B染色体标志基因。系统发育与序列分析进一步表明,PaChr24B.43因移码突变导致蛋白截短,可能已演化为假基因,但其在盐胁迫下仍表现出约5倍的表达量上调,提示其在非编码调控层面可能保留了功能意义;PaChr24B.82在其他植物物种中未检测到直系同源体,暗示其为B染色体特有的功能性新生基因。
山东大学生命科学学院已出站博士后王翠博士(兼职芬兰赫尔辛基大学)为第一作者,刘乐乐副研究员和郭卫华教授为共同通讯作者,山东大学生命科学学院为论文第一单位。赫尔辛基大学James Ord博士、上海辰山植物园颜梦晓博士、齐鲁师范学院蔡云飞博士、山东大学博士生邵弘锦、中国林业科学研究院林乐乐博士及赫尔辛基大学/南洋理工大学Jarkko Salojärvi助理教授参与了本研究并作出重要贡献。本研究得到了国家自然科学基金、山东省自然科学基金、芬兰树木生物学卓越中心的资助。
原文链接:https://link.springer.com/article/10.1186/s13059-026-04079-x
